决定这棵树倒塌的断线的算法?
通过比较4~9 bp长序列的位置权重矩阵(PWMs或PSSMs)的相似性(欧氏距离),建立了一棵纽尼克树。
该树的交互式版本在iTol (这里)上,您可以自由地使用它-在设置参数后按下“更新树”:
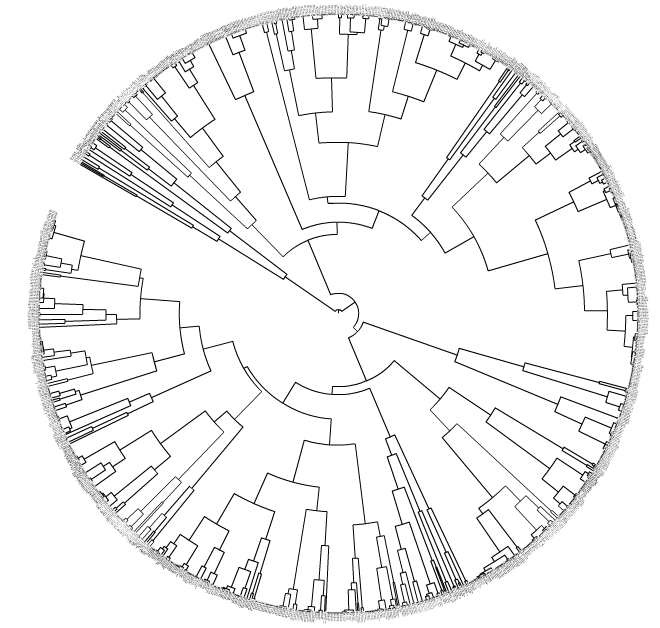
我的具体目标是:如果它们到最近的父类的平均距离是ETE2 Python包),则将它们(提示/终端节点/叶子)折叠在一起。这在生物学上是有趣的,因为一些基因调控的DNA基序可能是同源的(目录或同系物)。这种折叠可以通过上面链接的iTol图形用户界面来完成,例如,如果您选择X= 0.001,那么一些主题就会折叠成三角形(Motif族)。
我的问题:是否有人建议一种算法,可以输出或帮助可视化X的哪个值适合于“最大化崩溃的主题的生物学或统计相关性”?理想情况下,当用X绘制时,树的某些属性会发生一些明显的步骤变化,这意味着算法是明智的X。是否有任何已知的算法/脚本/包?也许代码会根据X的值绘制一些统计数据?我已经尝试过标出X和平均集群大小(matplotlib),但是我没有看到一个明显的“逐步增加”来告诉我要使用哪个X值:
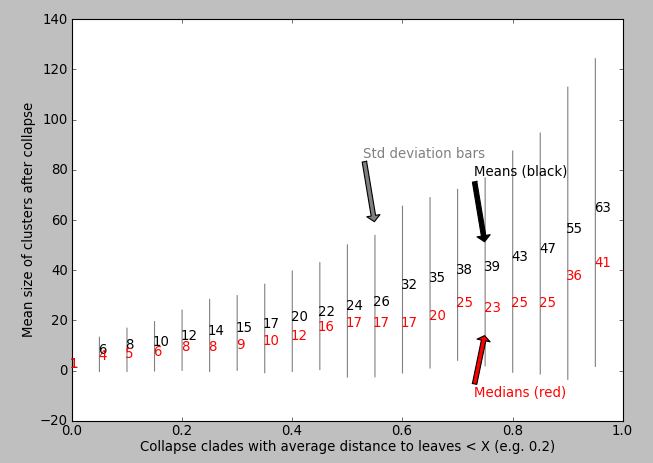
我的代码和数据:脚本的链接在这里,我对它进行了大量的注释,它将为您生成上面的树数据和图(使用参数d_from、d_to和d_step来探索距离截断,X)。如果您有简易安装和ete2,那么只需执行这两个bash命令就可以安装:
apt-get install python-setuptools python-numpy python-qt4 python-scipy python-mysqldb python-lxml
easy_install -U ete2回答 2
Stack Overflow用户
发布于 2014-12-28 13:26:39
正如Jeff提到的,您可以尝试使用类似于树协调的方法。但是标准的树和解实际上会失败。
协调首先需要在整个目标树中添加代表进化字符“损失”的分支。然后指示进化字符的“复制”发生的节点。损失和重复的加权和提供了一个优化的成本函数。
但在你的例子中,你想要解决的问题是“把这棵超级树分解成适当大小的正子树”。这意味着你不想像重复一样多的损失。你想要一种方法来打分这棵树,这样它就能显示出有多少个同源子树被合并到你的超级树中。因此,您可以尝试以下评分方法:
- 以一棵超级树为例,数数重复物种的数量,S1。
- 折叠所有的终端叶子,这是目录和计数的新数量的重复物种,S2。
- S1和S2之间的区别大约揭示了超级树中有多少子树。
- 纠正各种大小的超级树所造成的偏差,除以在超级树N中所代表的唯一物种的数量。
如果我们称这个分数为“子树因子”,那么它就等于:
S1 - S2 / N
推论:
- 如果S1 - S2 = S1,那么这意味着你的超级树中大约有一个真正的子树,所有多个物种的出现都是由于最近的目录。
- 如果S1 - S2 =0,则表示您的超级树中有近似S1真子树。
Stack Overflow用户
发布于 2014-05-08 06:48:48
我想我需要更多的了解才能给出具体的建议。但也许这会有帮助。我假设每个终端节点是一个序列,每个内部节点都是一个PSSM。
X的计算是特定于应用程序的。例如,当你想折叠所有同系物的时候,你得到的X和你想要折叠的X不一样。
由于基因是通过复制和物种化不断产生的,所以X没有一个值可以通过进化关系来区分序列。因此,我不认为您会找到一个令人满意的代理来确定序列之间的进化关系,只看集群统计数据。
一种更严格的方法是从每个调控基序的基因构建一棵基因树,并将其与一棵物种树相协调。这里有一些软件和其他的启发式方法,可以用来识别正方根/ inparalog。
如果您这样做,您的树的内部节点将被装饰由推断的进化事件(例如,复制,物种)。然后,你可以走到树上,为你不关心的类崩溃节点。
https://stackoverflow.com/questions/23346837
复制相似问题

