R语言 | GEO数据库的下载 以及表达矩阵和临床信息的提取
R语言 | GEO数据库的下载 以及表达矩阵和临床信息的提取
LN生物笔记
发布于 2023-02-23 11:18:29
发布于 2023-02-23 11:18:29
0.安装R包
如果是第一次使用,要先在RStudio里安装好这些包
install.packages("AnnoProbe")#用于下载GEO数据的包
BiocManager::install("GEOquery")#用于提取GEO数据中所含信息的包
BiocManager::install("limma")#用于差异分析的包
install.packages("tidyverse")1.载入R包
然后载入我们需要用到的包
library(AnnoProbe)#用于下载GEO数据的包
library(GEOquery)#从GEO数据集中提取表达矩阵或临床信息的包
library(tidyverse)2.利用AnnoProbe下载GEO数据库中的数据
以GSE14520数据系为例:
gset=AnnoProbe::geoChina('GSE14520')运行后,会得到一个叫做“gset”的对象,它是”list“数据类型
3.提取表达矩阵和临床信息
exprset <- data.frame(exprs(gset[[1]]))#exprs用于提取表达矩阵信息
expMatrix <- gset[[1]] pdata<-pData(exp)#pData用于提取临床信息gset[[1]] 的意思是,从gset这个对象中提取第一列数据。也就是提取了下图中$GSE16956_series_matrix.txt.... 这一列的数据
[[ ]]这个语法有点类似于,都是用来提取串列的。只不过[[]]可以提取list,而只能提取dataframe
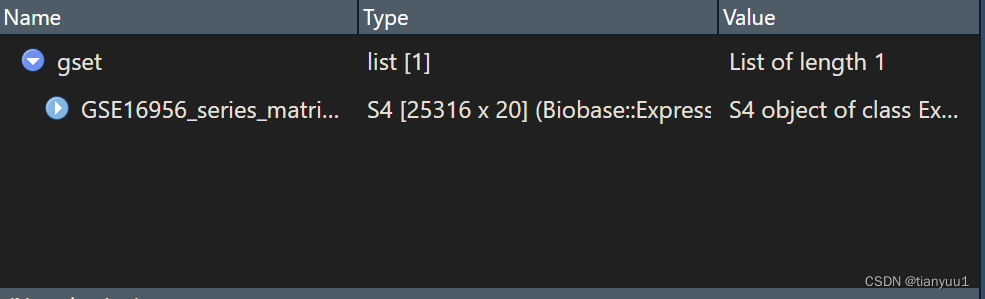
注意:
如果你的GSE只有一个GPL,那么从gset中就仅含有一列数据,也就是说gset[[1]]就能把这个GSE所有的数据提取出来。
但如果你的GSE只有两个GPL,那么从gset中就有两列数据,gset[[1]]只能提取该GSE中一个GPL,不注意这点就会遗漏掉另一个GPL的数据。所以,这种情况要使用两行代码分别提取两个GLP的数据。
expMatrix1 <- exprs(gset[[1]])#提取第一个平台的表达矩阵
expMatrix2 <- exprs(gset[[2]])#提取第二个平台的表达矩阵
expMatrix <- cbind(expMatrix1, expMatrix2)#两个表达矩阵合并为一个总矩阵
pdata1 <- pData(gset[[2]])#提取第一个平台的临床数据
pdata2 <- pData(gset[[1]])#提取第二个平台的临床数据那么如何判断你下载的这个GSE是有几个GPL呢?很简单,如果包含了两个或者多个GPL,你可以在RStudio右上角的环境变量中的”gset“后面的括号里看到”2 elements“的字样
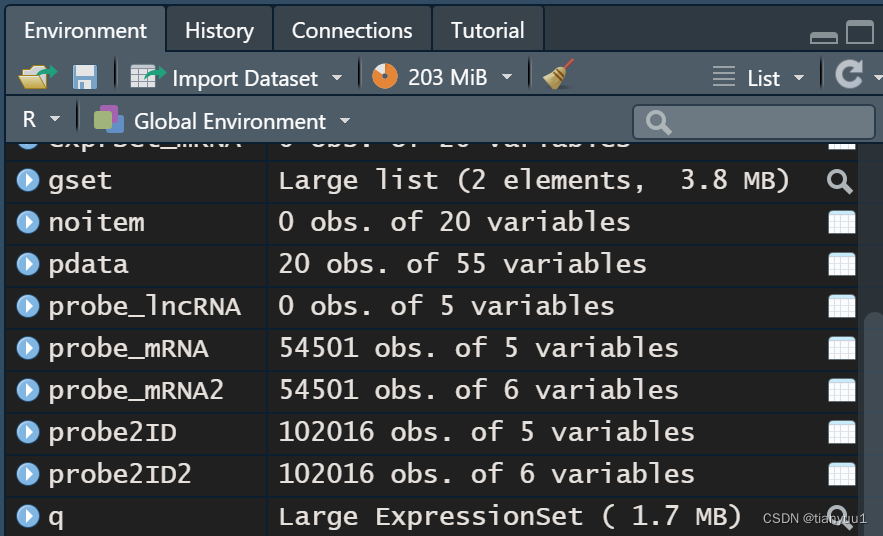
含有2个GPL的gset
如果只含有一个GPL,则不会显示括号,仅显示”Large ExpressionSet“的字样
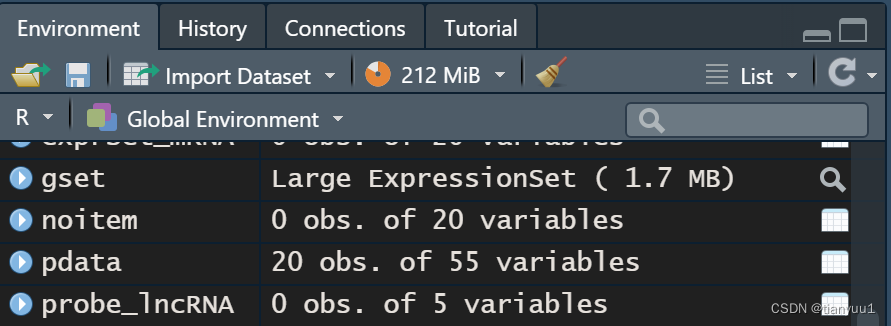
含有2个GPL的gset
或者你也可以通过View(gset)语法来查看:
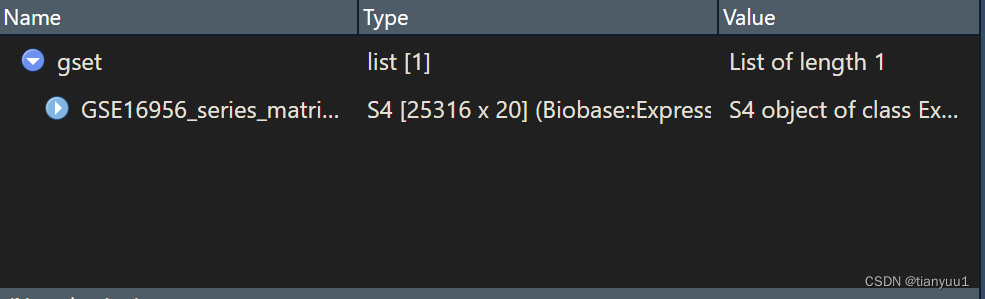
含有1个GPL的GSE
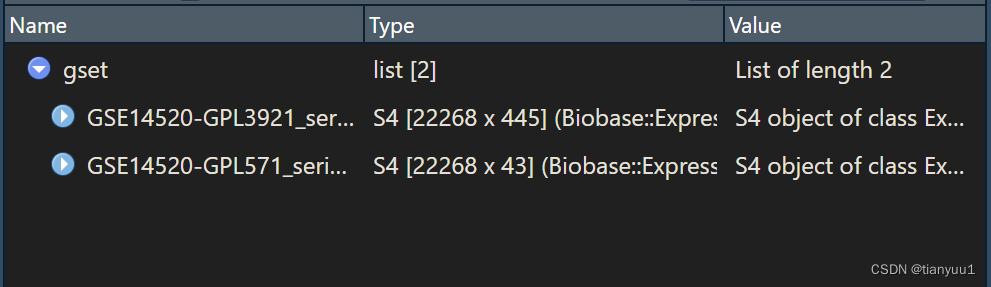
含有2个GPL的GSE
4.输出文件
最后将数据框输出为csv文件,这个时候如果直接用write.table()函数的话,会造成列名左移的情况,解决办法参见我之前的文章:(阅读全文)
https://blog.csdn.net/tianyuu1/article/details/128105158

本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2022-11-30,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读

