Nature 子刊 | 助力疾病研究,small RNA测序新技术:PSCSR-seq
Nature 子刊 | 助力疾病研究,small RNA测序新技术:PSCSR-seq

miRNA和其他形式的small RNA可以调节许多生物过程,单细胞small RNA测序可用于分析单个细胞的small RNA;然而,效率和规模的限制阻碍了它的广泛应用。近日Nature子刊《Scientific Reports》发表了一种small RNA测序新技术:平行单细胞smallRNA测序(parallel single-cell small RNA sequencing,PSCSR-seq),其克服了现有方法的局限性,并能够对单个细胞进行高通量small RNA表达谱分析。

small RNA测序工作流程涉及一系列反应:简言之,这些方法首先使用T4 RNA连接酶I/II将衔接子连接到small RNA分子上,从而使small RNA分子两侧有一个确定的序列。接下来,将连接的small RNA分子逆转录成cDNA并通过PCR进行扩增。现有的单细胞small RNA测序方法存在效率低的局限性,因为大多数测序reads来自适配器自连接(5'和3'适配器二聚体)或随机错误序列,并且靶miRNA reads通常较低。此外,这些方法的低通量设计不能实际应用于高度异质性组织样品的small RNA分析。
PSCSR-seq是什么?

基于此,研究团队开发了PSCSR-seq,其具有高度的灵敏度和可重复性,并且在多个领域具有优于现有方法的性能:1)PSCSR-seq大大缓解了单细胞small RNA测序的已知问题,如自连接二聚体比例高,miRNA reads比例低。2)PSCSR-seq是一个高效的系统。其适配器经过精心设计,以确保与其他适配器相比具有更高的连接效率和更低的副产物形成。该系统不需要额外的试剂,如PEG或核糖体RNA掩蔽寡核苷酸。3)PSCSR-seq是以纳升规模和高通量样品管理系统为基础进行的。纳升规模的反应可以提高反应物的浓度,降低试剂的成本。而且,在纳米孔芯片中的所有分析都是在相同的反应条件下进行的,可以减少反应变化。
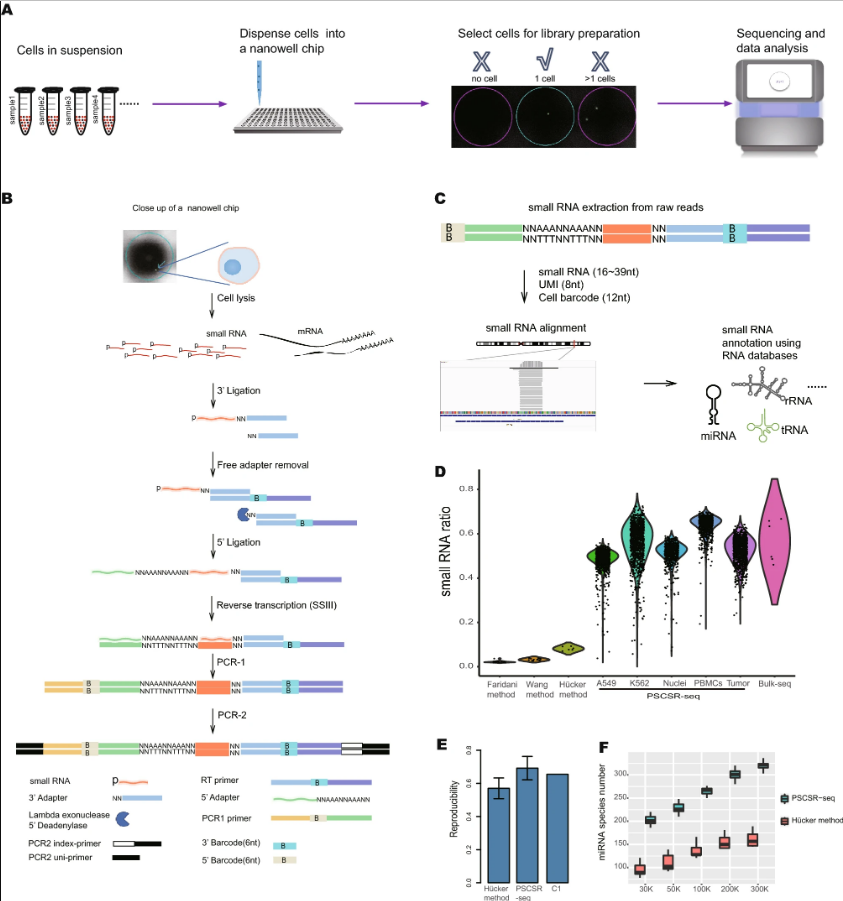
用PSCSR-seq进行高质量的单细胞small RNA测序
PSCSR-seq的性能测试结果

开发团队应用PSCSR-seq分析培养细胞的small RNA 图谱,然后分离细胞核和 PBMC 进行实验验证。此外,还研究了肺癌样本中的small RNA 图谱。

对PSCSR-seq数据的分析表明,可以根据miRNA的表达模式来确定不同的细胞类型,并显示细胞核中的miRNA含量是有参考价值的(例如,在分离的细胞核中可以检测到细胞类型标记的miRNA)。
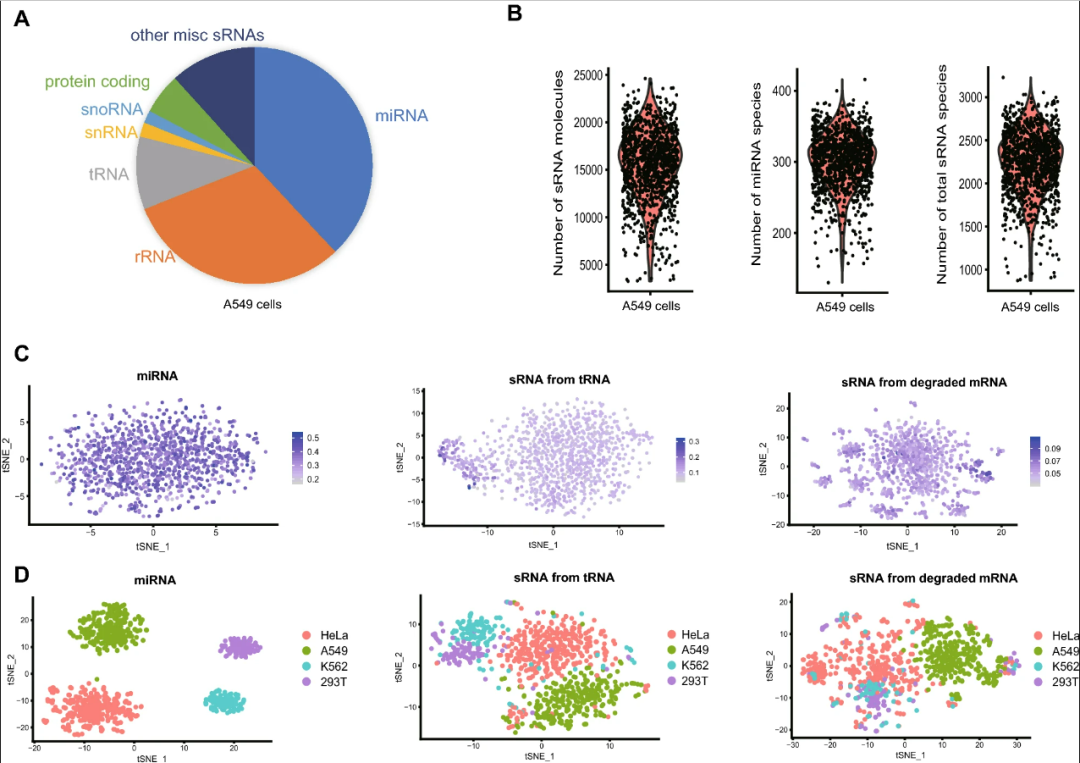
通过PSCSR-seq对培养细胞进行small RNA分析
PSCSR-seq非常敏感:仅对732个外周血单核细胞(PBMCs)的分析就能检测到774个miRNA,而bulk small RNA分析需要从大约106个细胞中输入RNA才能检测到这么多miRNA。同时,开发团队确定了42个miRNAs作为PBMC亚群的标志物。
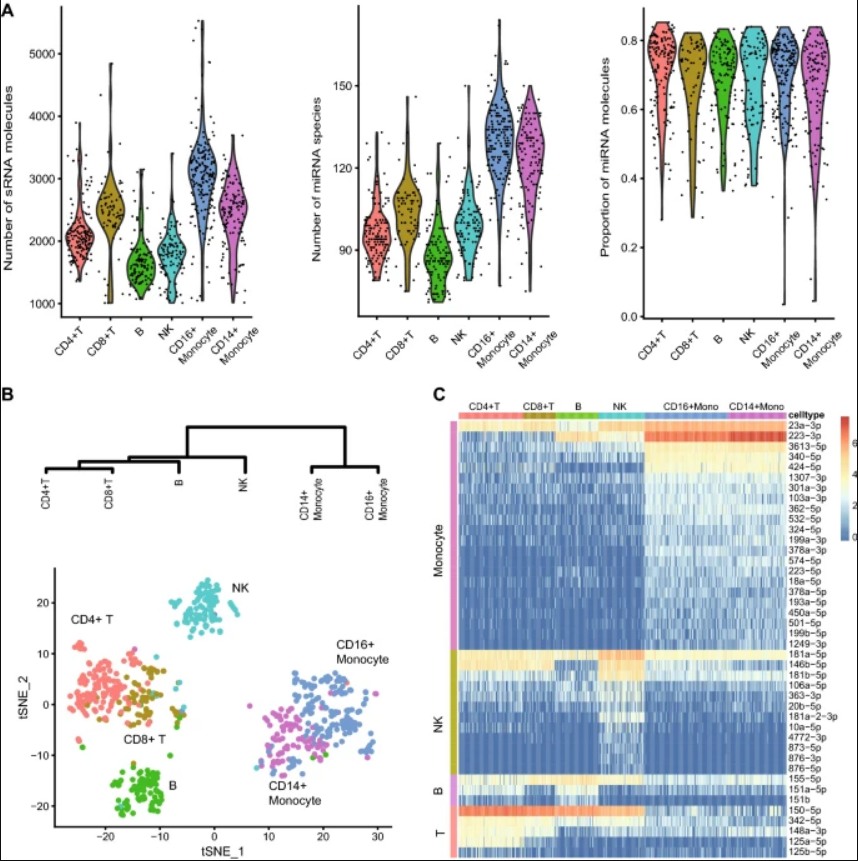
使用PSCSR-seq对PMBC进行small RNA分析
开发团队分析了来自肺癌活检的9,533个细胞的miRNA谱,通过剖析细胞亚群,确定了肺癌潜在诊断和治疗的miRNAs。
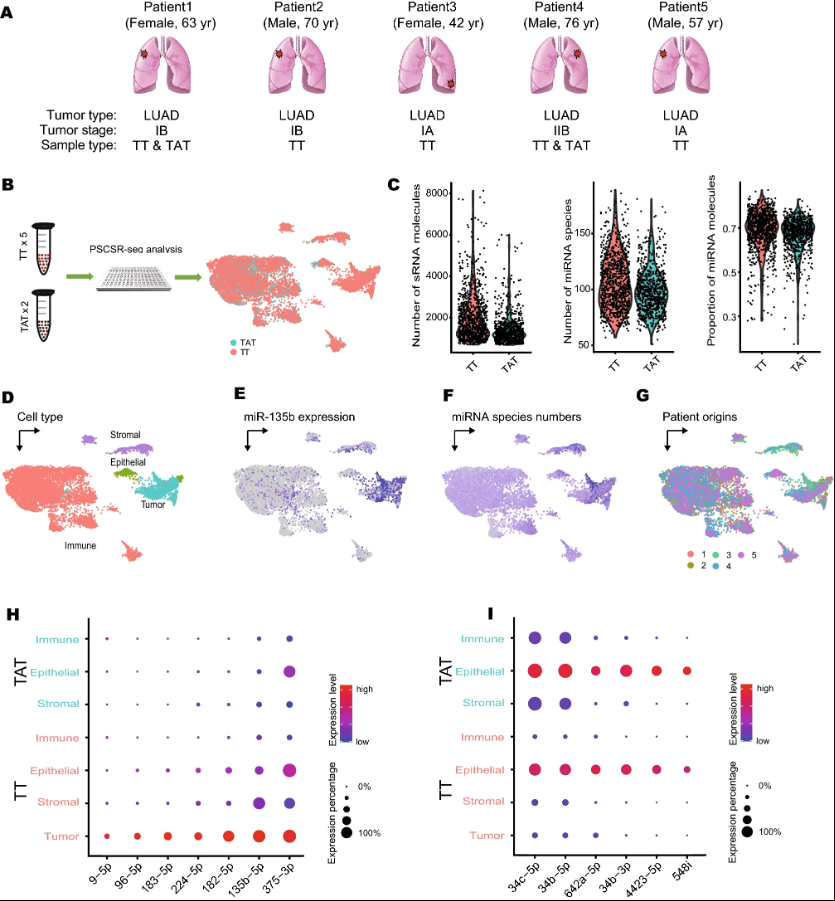
通过PSCSR-seq对肺腺癌进行miRNA分析
综上所述,PSCSR-seq具有高度的敏感性和可重复性,从而使其成为癌症和生命科学研究中miRNA分析的先进工具。PSCSR-seq所有源代码都在GitHub中可用(👉 可点击阅读原文访问):
https://github.com/biocaitao/PSCSR-seq.
