Nature子刊 | SComatic:从头检测高通量单细胞数据集中的体细胞突变
Nature子刊 | SComatic:从头检测高通量单细胞数据集中的体细胞突变

单细胞分辨率的体细胞突变特征分析对于研究癌症演化、克隆嵌合以及细胞可塑性至关重要。近日,《Nature Biotechnology》发表了一种用于直接检测单细胞转录组和ATAC-seq数据集中的体细胞突变的算法——SComatic。

SComatic是什么?

SComatic是一种在单细胞图谱数据集中从头检测体细胞SNV的算法,不需要匹配的批量或单细胞DNA测序数据。SComatic利用对非肿瘤样本参数化的过滤器和统计检验,将体细胞突变与多态性、RNA编辑事件和Artefacts分开来。
简而言之,SComatic利用通过标记基因表达等建立的细胞类型注释,计算来自同一个体的不同细胞类型的基因组每个位置的碱基计数。体细胞突变与种系多态性和伪变异通过一组硬过滤器和统计检验区分开来。
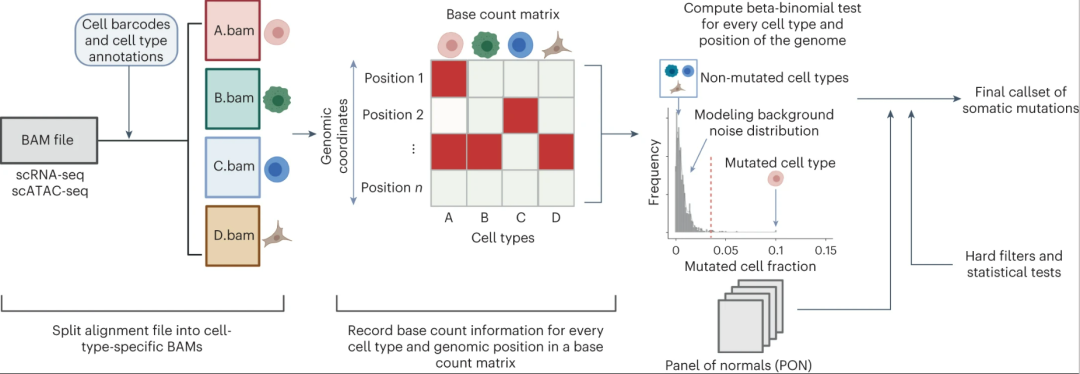
SComatic概述
SComatic的性能测试

开发团队利用已发表的来自622个样本的scRNAs-seq数据和来自66个样本的scATAC-seq数据,总计2,655,775个非肿瘤细胞和癌细胞,研究表明:与现有的算法相比,SComatic在不同的癌症数据集中具有更高的体细胞SNVs调用精度。此外,SComatic允许在细胞类型分辨率下检测突变负担和从头发现突变特征,即使是分化的细胞和来自多克隆组织的细胞,也表现出高度的遗传异质性。
在scRNA-seq中通过scoatic和WES检测到的突变之间存在高度一致性,并强调了基于基因组测序数据中先前发现的突变的基因分型来调用单细胞数据中的突变的方法,对于具有高度遗传异质性的样本可能具有较低的灵敏度。
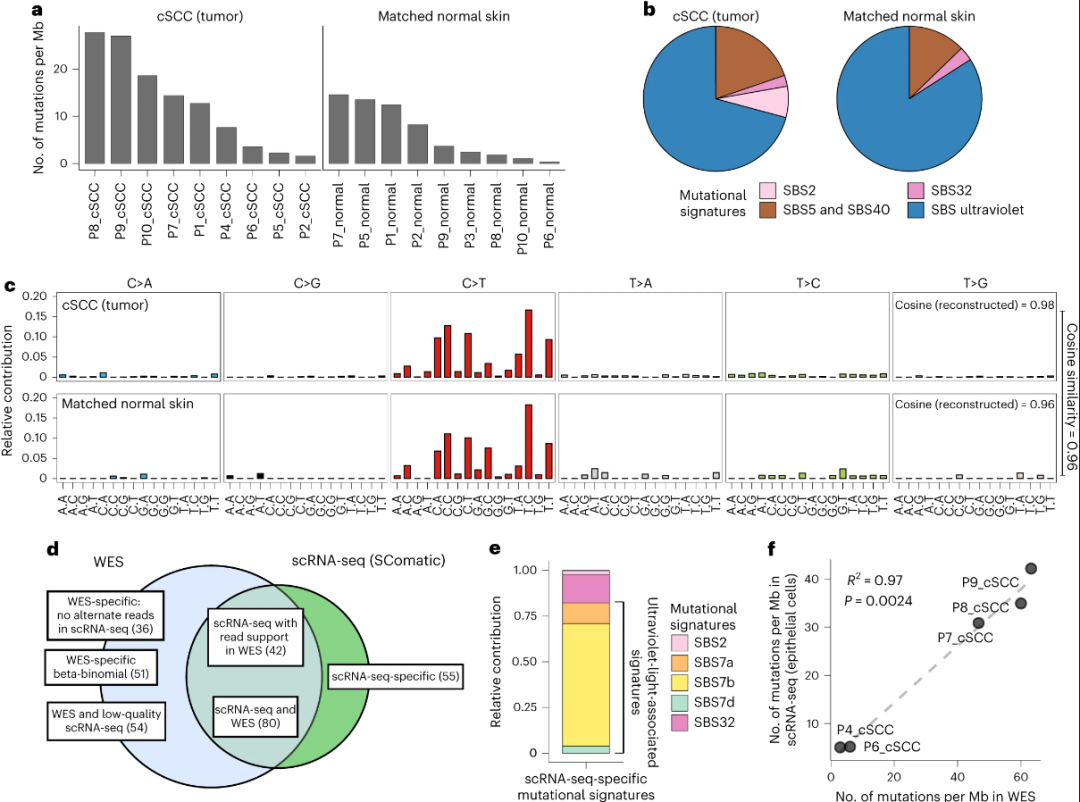
使用匹配的scRNA-seq和外显子组测序数据验证SComatic
现有的scRNA-seq数据体细胞突变检测方法具有较高的假阳性率,而SComatic 能够以单细胞分辨率高精度检测体细胞突变。此外,SComatic的更高性能不仅是由过滤掉常见的SNPs驱动的,而且是由背景错误率的准确建模驱动的,这有助于以高精度区分Artefacts和真实突变。
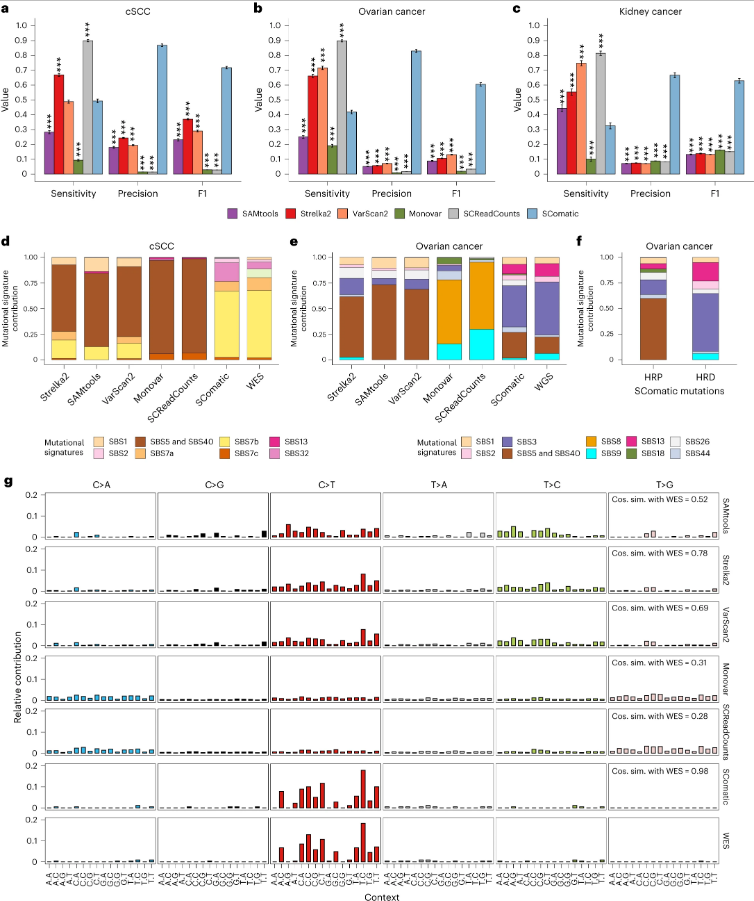
SComatic与其他突变检测方法的性能比较
SComatic可在单细胞分辨率下鉴定高突变样本中的突变过程,而不需要匹配的基因组测序数据。
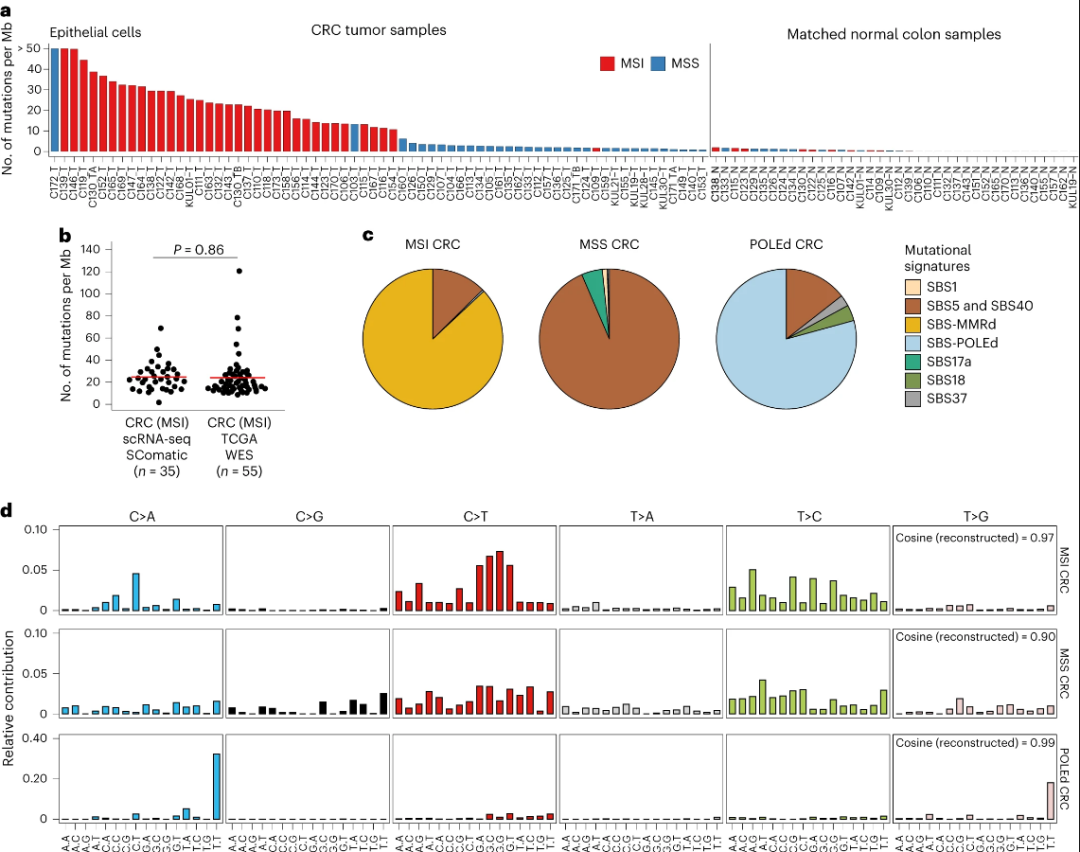
检测结直肠癌样本scRNA-seq数据中的体细胞突
SComatic允许研究多克隆组织中的突变模式和突变率。
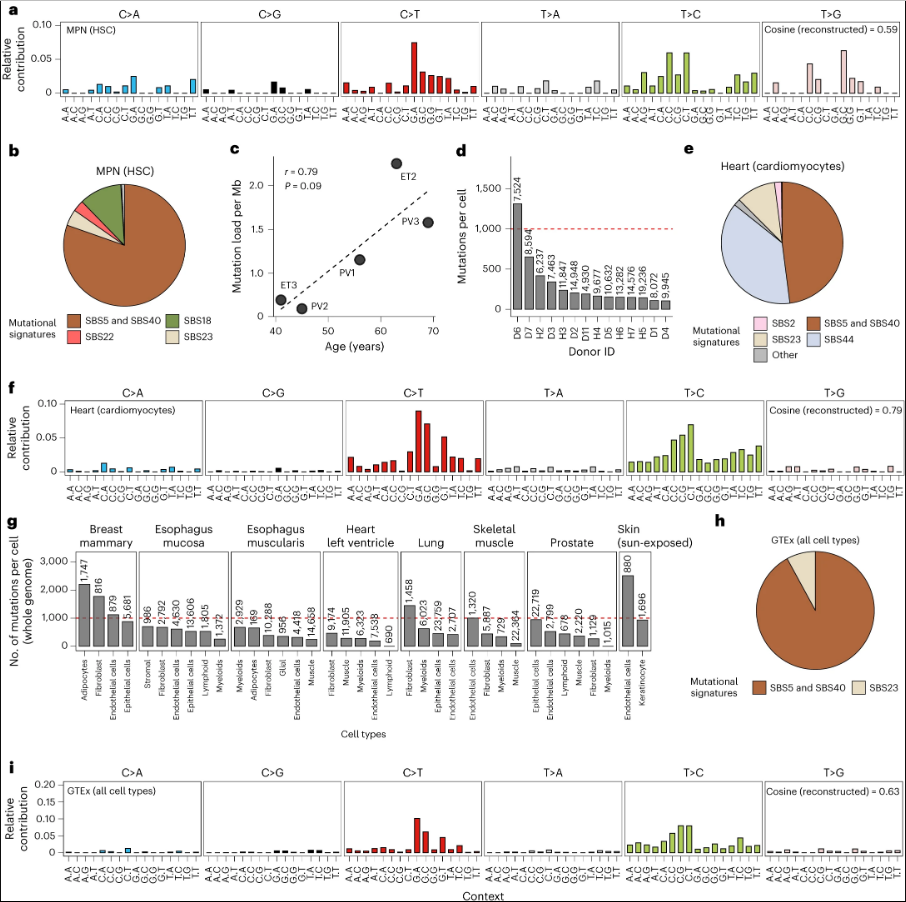
在肿瘤突变负荷较低的样本中检测体细胞突变
SComatic可以发现亚克隆驱动突变。
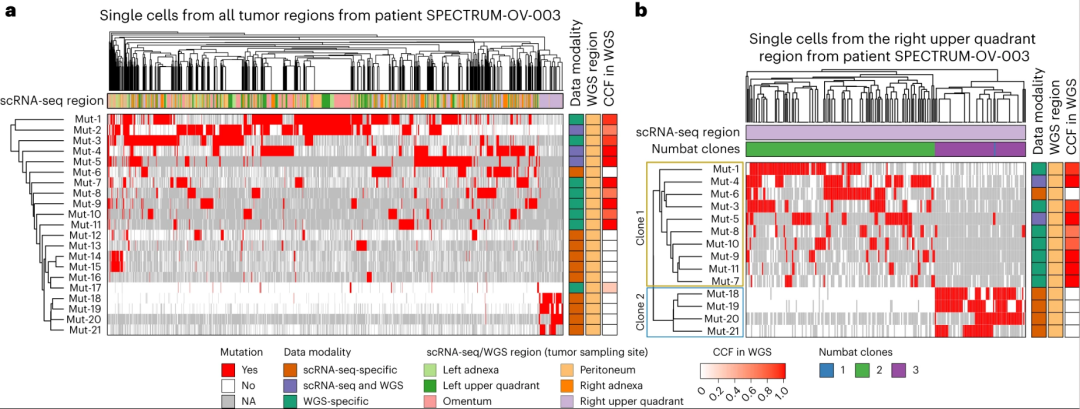
利用SComatic在卵巢癌患者scRNA-seq数据中检测到的体细胞突变分析肿瘤内异质性
尽管SComatic性能较高,但受限于当前单细胞测序分析的稀疏性和低测序深度。随着单细胞方法的改进,SComatic将能够从单细胞数据集中获得进一步的见解。总之,SComatic为利用大规模计划(如人类细胞图谱或人类肿瘤图谱网络)下产生的单细胞数据集研究人类以及其他生物的体细胞诱变提供了可能性。
SComatic用Python 3实现,代码已存入Github(👉 点击阅读原文访问):https://github.com/cortes-ciriano-lab/SComatic.
//
建议对技术细节感兴趣的小伙伴请参考文献原文~
对于文献整理过程中有翻译不当或错误也欢迎大家在评论区留言指出,互相交流学习!
Muyas, F., Sauer, C.M., Valle-Inclán, J.E. et al. De novo detection of somatic mutations in high-throughput single-cell profiling data sets. Nat Biotechnol (2023). https://doi.org/10.1038/s41587-023-01863-z
